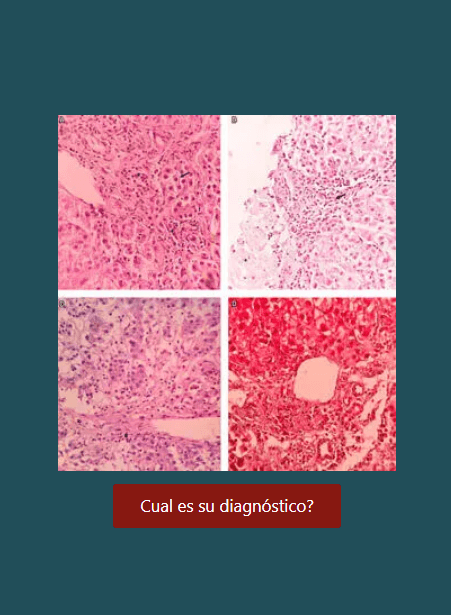
Genotipificación de cagA y de la región intermedia de vacA en cepas de Helicobacter pylori aisladas de pacientes adultos colombianos y asociación con enfermedades gástricas
DOI:
https://doi.org/10.22516/25007440.168Palabras clave:
Helicobacter pylori, cagA, vacAResumen
Objetivo: este estudio caracteriza la diversidad de los genes de virulencia cagA (gen asociado con la citotoxina A) y vacA (citotoxina vacuolizante) en pacientes colombianos para determinar posibles asociaciones entre estos 2 genes y la severidad de los hallazgos endoscópicos teniendo en cuenta todos los genotipos reportados para el gen vacA (s, m e i).
Materiales y métodos: Helicobacter pylori fue detectado por cultivo y por métodos moleculares en biopsias de 62 pacientes. Los genotipos de cagA y vacA (m/i/s) se determinaron por reacción en cadena de la polimerasa (PCR) y secuenciación. Resultados: se aislaron 124 cepas de 62 pacientes; de estas, el 48,5% (n = 48) fueron vacA s2/m2/i2-cagA (-) presente en su mayoría en pacientes con gastritis folicular; mientras el 32,3% (n = 32) fueron vacA s1/m1/i1-cagA (+) presentes mayormente en pacientes con gastritis folicular, gastritis crónica y posible metaplasia. Se encontró una asociación significativa entre la presencia de cagA y el genotipo vacA s1/m1/i1 y la ausencia de cagA y el genotipo vacA s2/m2/i2 (p <0,001). No se encontró una asociación significativa entre la severidad de los hallazgos endoscópicos y el estatus cagA-vacA de las cepas.
Conclusión: se encontró una baja prevalencia de cepas cagA (+), el estatus cagA-vacA no es un predictor de riesgo en la población estudiada y la presencia de infecciones heterogéneas sin tropismo sugieren la necesidad de tomar biopsias tanto del cuerpo como del antro del estómago en la práctica clínica rutinaria.
Descargas
Lenguajes:
esAgencias de apoyo:
Universidad de los Andes, Facultad de Ciencias, code, P16.160322.001/01-BIO01, beca de investigación del DFG (JI 221/1-1) para LFJ-SReferencias bibliográficas
Peleteiro B, Bastos A, Ferro A, et al. Prevalence of Helicobacter pylori infection worldwide: a systematic review of studies with national coverage. Dig Dis Sci. 2014;59(8):1698-709. doi: 10.1007/s10620-014-3063-0.
Rhead JL, Letley DP, Mohammadi M, et al. A new Helicobacter pylori vacuolating cytotoxin determinant, the intermediate region, is associated with gastric cancer. Gastroenterology. 2007;133(3):926-36. doi: 10.1053/j.gastro.2007.06.056.
Jones KR, Jang S, Chang JY, et al. Polymorphisms in the intermediate region of VacA impact Helicobacter pylori-induced disease development. J Clin Microbiol. 2011;49(1):101-10. doi: 10.1128/JCM.01782-10.
García CA, Barra TR, Delgado SC, et al. Genotipificación de aislados clínicos de Helicobacter pylori en base a genes asociados a virulencia cagA, vacA y babA2: primer aislamiento de una cepa babA2 positiva en pacientes chilenos. Rev Médica Chile. 2006;134(8):981-8. doi: 10.4067/S0034-98872006000800006.
Cover TL, Blaser MJ. Purification and characterization of the vacuolating toxin from Helicobacter pylori. J Biol Chem. 1992;267(15):10570-5.
Kim I-J, Blanke SR. Remodeling the host environment: modulation of the gastric epithelium by the Helicobacter pylori vacuolating toxin (VacA). Front Cell Infect Microbiol. 2012;2:37. doi: 10.3389/fcimb.2012.00037.
Foo JH, Culvenor JG, Ferrero RL, et al. Both the p33 and p55 Subunits of the Helicobacter pylori VacA Toxin Are Targeted to Mammalian Mitochondria. J Mol Biol. 2010;401(5):792-8. doi: 10.1016/j.jmb.2010.06.065.
Jain P, Luo Z-Q, Blanke SR. Helicobacter pylori vacuolating cytotoxin A (VacA) engages the mitochondrial fission machinery to induce host cell death. Proc Natl Acad Sci U S A. 2011;108(38):16032-7. doi: 10.1073/pnas.1105175108.
Nakayama M, Kimura M, Wada A, et al. Helicobacter pylori VacA Activates the p38/Activating Transcription Factor 2-mediated Signal Pathway in AZ-521 Cells. J Biol Chem. 2004;279(8):7024-8. doi: 10.1074/jbc.M308898200.
Boncristiano M, Paccani SR, Barone S, et al. The Helicobacter pylori vacuolating toxin inhibits T cell activation by two independent mechanisms. J Exp Med. 2003;198(12):1887-97. doi: 10.1084/jem.20030621.
Chung C, Olivares A, Torres E, et al. Diversity of vacA intermediate region among Helicobacter pylori strains from several regions of the world. J Clin Microbiol. 2010;48(3):690-6. doi: 10.1128/JCM.01815-09.
Ferreira RM, Machado JC, Letley D, et al. A novel method for genotyping the Helicobacter pylori vacA Intermediate region directly in gastric biopsy specimens. J Clin Microbiol. 2012;50(12):3983-9. doi: 10.1128/JCM.02087-12.
González-Rivera C, Algood HMS, Radin JN, et al. The intermediate region of Helicobacter pylori vacA is a determinant of toxin potency in a jurkat t cell assay. Infect Immun. 2012;80(8):2578-88. doi: 10.1128/IAI.00052-12.
Agah S, Khedmat H, Ghamar-Chehred ME, et al. Female gender and Helicobacter pylori infection, the most important predisposition factors in a cohort of gastric cancer: a longitudinal study. Casp J Intern Med. 2016;7(2):136-41.
Naja F, Kreiger N, Sullivan T. Helicobacter pylori infection in Ontario: Prevalence and risk factors. Can J Gastroenterol. 2007;21(8):501-6. doi: 10.1155/2007/462804.
Zhu Y, Zhou X, Wu J, et al. Risk factors and prevalence of Helicobacter pylori infection in persistent high incidence area of gastric carcinoma in Yangzhong City. Gastroenterol Res Pract. 2014;2014:e481365.
Jiménez-Soto LF, Rohrer S, Jain U, et al. Effects of cholesterol on Helicobacter pylori growth and virulence properties in vitro. Helicobacter. 2012;17(2):133-9. doi: 10.1111/j.1523-5378.2011.00926.x.
Ménard A, Santos A, Mégraud F, et al. PCR-restriction fragment length polymorphism can also detect point mutation A2142C in the 23S rRNA gene, associated with Helicobacter pylori resistance to clarithromycin. Antimicrob Agents Chemother. 2002;46(4):1156-7. doi: 10.1128/AAC.46.4.1156-1157.2002.
Secka O, Antonio M, Berg DE, et al. Mixed infection with cagA positive and cagA negative strains of Helicobacter pylori lowers disease burden in The Gambia. PLoS ONE. 2011;6(11):e27954. doi: 10.1371/journal.pone.0027954.
R Development Core Team. R: A language and environment for statistical computing. R Foundation for Statistical Computing [internet] 2008 [acceso el 24 de noviembre de 2016]. Disponible en: http://www.R-project.org.
Argent RH, Thomas RJ, Letley DP, et al. Functional association between the Helicobacter pylori virulence factors vacA and cagA. J Med Microbiol. 2008;57(2):145-50. doi: 10.1099/jmm.0.47465-0.
Jang S, Jones KR, Olsen CH, et al. Epidemiological link between gastric disease and polymorphisms in vacA and cagA. J Clin Microbiol. 2010;48(2):559-67. doi: 10.1128/JCM.01501-09.
Yamazaki S, Yamakawa A, Okuda T, et al. Distinct Diversity of vacA, cagA, and cagE Genes of Helicobacter pylori Associated with Peptic Ulcer in Japan. J Clin Microbiol. 2005;43(8):3906-16. doi: 10.1128/JCM.43.8.3906-3916.2005.
Quiroga AJ, Cittely DM, Bravo MM. Frecuencia de los genotipos babA2, oipA y cagE de Helicobacter pylori en pacientes colombianos con enfermedades gastroduodenales. Biomédica. 2005;25:325-34. doi: 10.7705/biomedica.v25i3.1357.
Molina Delgado A, Jaramillo Henao C, Delgado Perafán M, et al. Detección y genotipificación de Helicobacter pylori sobre la base de los genes ADNr 16S y el gen asociado a citotoxina (cagA) y posible asociación con enfermedades gastrointestinales. Rev ista Cubana de Medicina Tropical. 2008;60:105-10.
Basso D, Zambon C-F, Letley DP, et al. Clinical relevance of Helicobacter pylori cagA and vacA gene polymorphisms. Gastroenterology. 2008;135(1):91-9. doi: 10.1053/j.gastro.2008.03.041.
Parente JML, da Silva BB, Palha-Dias MPS, et al. Helicobacter pylori infection in children of low and high socioeconomic status in northeastern Brazil. Am J Trop Med Hyg. 2006;75(3):509-12.
Ramírez Ramos A, Chinga Alayo E, Mendoza Requena D, et al. Variación de la prevalencia del H. pylori en el Perú período (1985-2002), en una población de nivel socioeconómico medio y alto. Rev Gastroenterol Perú. 2003;23(2):92-8.
Mendoza-Elizalde S, Cortés-Márquez AC, Giono-Cerezo S, et al. Analysis of the genotypic diversity of strains of Helicobacter pylori isolated from pediatric patients in Mexico. Infect Genet Evol. 2015;29:68-74. doi: 10.1016/j.meegid.2014.11.002.
Pinto-Ribeiro I, Ferreira RM, Batalha S, et al. Helicobacter pylori vacA genotypes in chronic gastritis and gastric carcinoma patients from Macau, China. Toxins (Basel). 2016;8(5). pii: E142. doi: 10.3390/toxins8050142.
Atherton JC, Cao P, Peek RM Jr, et al. Mosaicism in vacuolating cytotoxin alleles of Helicobacter pylori. Association of specific vacA types with cytotoxin production and peptic ulceration. J Biol Chem. 1995;270(30):1-7. doi: 10.1074/jbc.270.30.17771.
Nagiyev T, Yula E, Abayli B, et al. Prevalence and genotypes of Helicobacter pylori in gastric biopsy specimens from patients with gastroduodenal pathologies in the Cukurova Region of Turkey. J Clin Microbiol. 2009;47(12):4150-3. doi: 10.1128/JCM.00605-09.
Breurec S, Michel R, Seck A, et al. Clinical relevance of cagA and vacA gene polymorphisms in Helicobacter pylori isolates from Senegalese patients. Clin Microbiol Infect. 2011;18(2):153-9. doi: 10.1111/j.1469-0691.2011.03524.x.
Bravo MM, Trujillo E, Quiroga A, et al. Genotipificación de Helicobacter pylori en individuos de dos regiones de Colombia con riesgo de cáncer gástrico opuesto. Rev Colomb Cancerol. 2013;17(4):178-9.
Nogueira C, Figueiredo C, Carneiro F, et al. Helicobacter pylori genotypes may determine gastric histopathology. Am J Pathol. 2001;158(2):647-54. doi: 10.1016/S0002-9440(10)64006-0.
Muñoz-Ramírez ZY, Mendez-Tenorio A, Kato I, et al. Whole genome sequence and phylogenetic analysis show Helicobacter pylori strains from Latin America have followed a unique evolution pathway. Front Cell Infect Microbiol. 2017;7:50. doi: 10.3389/fcimb.2017.00050.
Ossa H, Aquino J, Pereira R, et al. Outlining the ancestry landscape of Colombian admixed populations. PLoS One. 2016;11(10):e0164414. doi: 10.1371/journal.pone.0164414.
Descargas
Publicado
Cómo citar
Número
Sección
Licencia
Aquellos autores/as que tengan publicaciones con esta revista, aceptan los términos siguientes:
Los autores/as ceden sus derechos de autor y garantizarán a la revista el derecho de primera publicación de su obra, el cuál estará simultáneamente sujeto a la Licencia de reconocimiento de Creative Commons que permite a terceros compartir la obra siempre que se indique su autor y su primera publicación en esta revista.
Los contenidos están protegidos bajo una licencia de Creative Commons Reconocimiento-NoComercial-SinObraDerivada 4.0 Internacional.

| Estadísticas de artículo | |
|---|---|
| Vistas de resúmenes | |
| Vistas de PDF | |
| Descargas de PDF | |
| Vistas de HTML | |
| Otras vistas | |